Mostra il codice R
meanSdPlot(assay(dds), ranks = FALSE)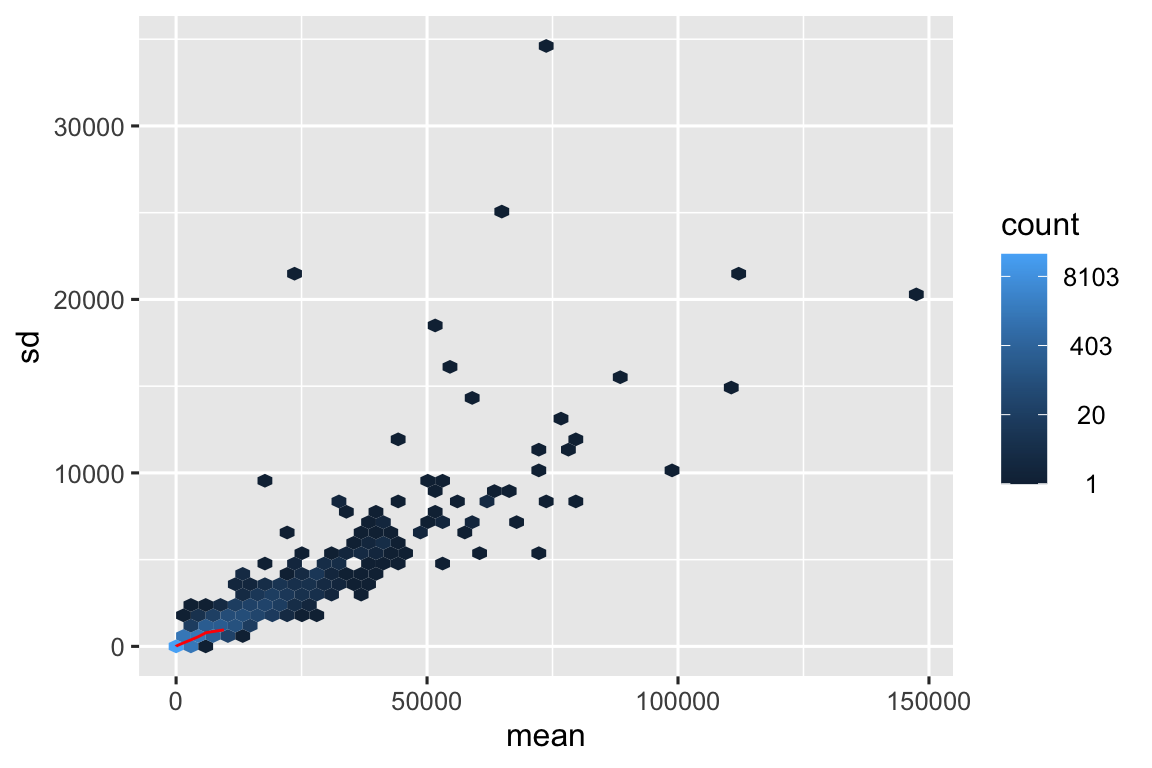
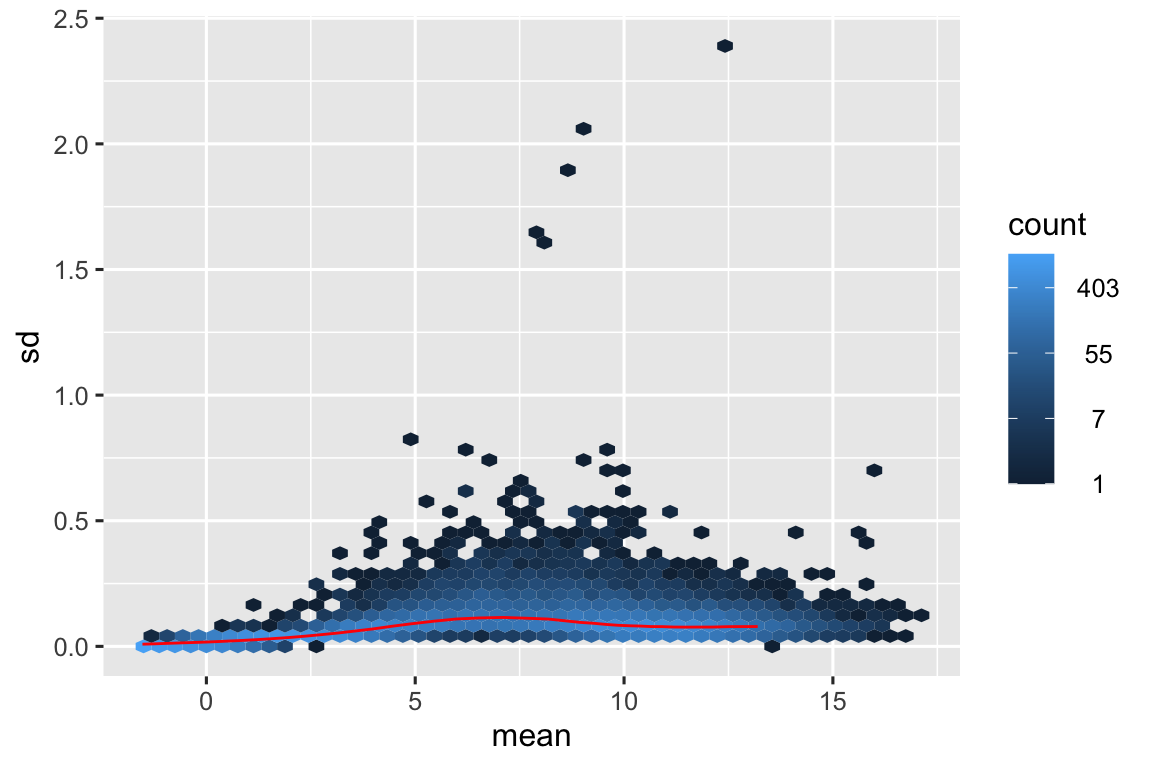
meanSdPlot(assay(dds), ranks = FALSE)
Un grafico Media/DS (Deviazione Standard) è uno strumento utile per valutare l’efficacia dei metodi di normalizzazione dell’abbondanza genica, specialmente nell’analisi dei dati RNA-Seq. Ecco come funziona:
1. Le basi
2. Costruire il grafico
3. Interpretazione
4. Perché è importante
Esempio:
Immagina un grafico Media/DS in cui la deviazione standard è molto più alta per i geni con espressione media elevata. Ciò suggerisce un bias correlato alla profondità di sequenziamento o alla lunghezza del gene. Un buon metodo di normalizzazione dovrebbe ridurre questa tendenza, portando a una distribuzione più uniforme delle deviazioni standard su tutti i livelli di espressione.
In sintesi: Il grafico Media/DS è uno strumento diagnostico visivo che ti aiuta a valutare la qualità della normalizzazione dell’abbondanza genica. È un passaggio chiave per garantire l’accuratezza e l’affidabilità delle analisi a valle come l’espressione genica differenziale.
Per stabilizzare la varianza e rendere i dati più adatti alle assunzioni del modello statistico, possiamo applicare trasformazioni come la Variance Stabilizing Transformation (VST) o la Regularized Log Transformation (rlog). La scelta della trasformazione dipenderà dalle caratteristiche dei dati e dagli obiettivi dell’analisi.
Sia la VST (Variance Stabilizing Transformation) che la rlog (Regularized Log Transformation) mirano a trasformare i dati di conteggio per stabilizzare la varianza tra i geni con diversa espressione.
rlog <- DESeq2::rlog(dds, blind = TRUE)
meanSdPlot(assay(rlog), ranks = FALSE)